MIND(Morphometric INverse Divergence, Sebenius et al., 2023)和MSN(Morphometric Similarity Network, Seidlitz et al., 2018)是基于T1加权结构像构建结构相似性网络的两种主流方法。那么,在实际研究中,究竟该选择哪种方法来构建网络呢?Sebenius等人(2023)发现,与MSN相比,MIND方法构建的脑网络具有更高的生物有效性,且对年龄的预测能力更强,这初步表明MIND可能在某些方面优于MSN。我们近期完成的研究(Gao & Hu, 2026)则从两个关键维度对两种方法进行了系统比较:重测信度和年龄敏感性。
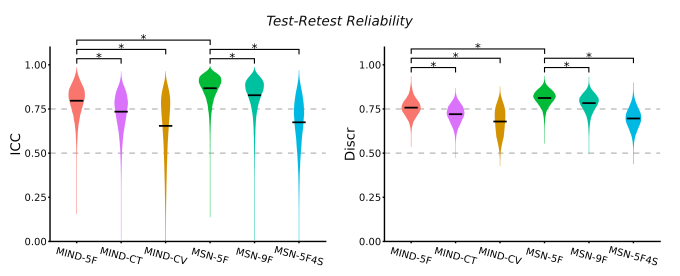
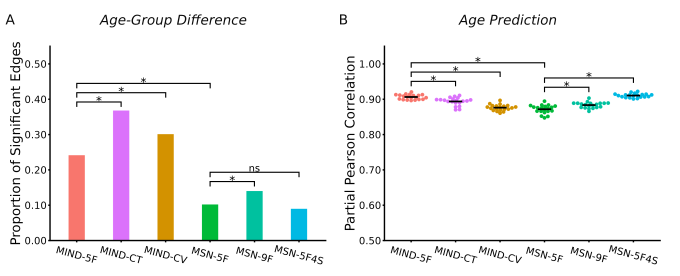
重测信度反映了一种方法或测量的稳定性。如果同一方法在重复测量中产生波动较大的结果,那么该方法就缺乏可靠性。然而,重测信度只是方法学评估的基础,更重要的是,一种好的方法应能准确捕捉与生物学相关的个体差异。为此,我们选择年龄作为参照标准,主要基于两点考虑:一是年龄数据易于获取,二是已有大量研究证实脑结构与年龄密切相关,使年龄成为理想的方法学比较基准。我们从两个角度评估年龄敏感性:(1)将年龄作为连续变量,考察网络特征对年龄的预测准确性;(2)比较老年组与青年组在网络连接上的组间差异。
此外,Sebenius等人(2023)在构建MIND网络时使用了五个形态学特征(皮层厚度、表面积、灰质体积、沟深和平均曲率),但并未对为何选择这五个特征提供充分解释。因此,我们在研究中还探讨了不同形态学特征组合对结果的影响,以考察特征选择的稳健性。
通过对多个公开数据集的分析,我们得到了以下可重复的主要发现:
- 重测信度方面,在使用相同五个特征时,MSN优于MIND(图1);
- 年龄敏感性方面,在使用相同五个特征时,MIND优于MSN(图2);
- 特征选择对MIND和MSN的重测信度及年龄敏感性均有显著影响(图1和图2);
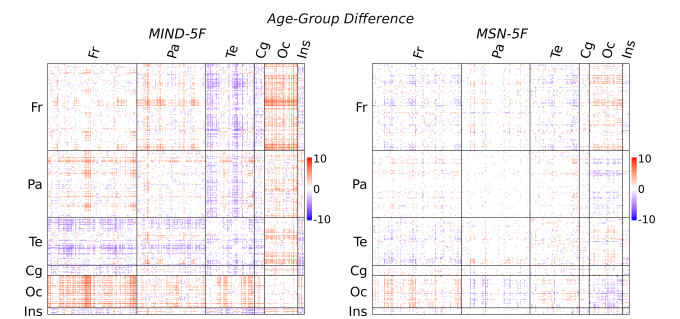
- 在老年组与青年组的比较中,MIND和MSN呈现出不同的空间分布模式,这可能暗示两种方法对应不同的神经生理机制(图3);
- 对于MIND方法,若研究目的为单条连接水平的组间比较,使用单个形态学特征可能更具优势(图2A);而对于MSN方法,若研究目的为基于机器学习的预测,则使用更多特征效果可能更佳(图2B)。
我们希望这些发现能够为研究者在选择结构相似性网络构建方法时提供有价值的参考。
参考文献
- Sebenius, I., Seidlitz, J., Warrier, V., Bethlehem, R. A. I., Alexander-Bloch, A., Mallard, T. T., Garcia, R. R., Bullmore, E. T., & Morgan, S. E. (2023). Robust estimation of cortical similarity networks from brain MRI. Nature neuroscience, 26(8), 1461–1471. https://doi.org/10.1038/s41593-023-01376-7
- Seidlitz, J., Váša, F., Shinn, M., Romero-Garcia, R., Whitaker, K. J., Vértes, P. E., Wagstyl, K., Kirkpatrick Reardon, P., Clasen, L., Liu, S., Messinger, A., Leopold, D. A., Fonagy, P., Dolan, R. J., Jones, P. B., Goodyer, I. M., NSPN Consortium, Raznahan, A., & Bullmore, E. T. (2018). Morphometric Similarity Networks Detect Microscale Cortical Organization and Predict Inter-Individual Cognitive Variation. Neuron, 97(1), 231–247.e7. https://doi.org/10.1016/j.neuron.2017.11.039
- Gao, J., & Hu, Y. (2026). MIND versus MSN: A systematic evaluation of test-retest reliability and age sensitivity for T1-weighted structural similarity networks. Network Neuroscience. Advance online publication. https://doi.org/10.1162/NETN.a.553

“MIND与MSN的比较:重测信度与年龄敏感性”上的4条回复
很有代表性的研究成果!意义深远!
抱歉没有及时回复,网站邮件提醒出了点问题。感谢您的鼓励和认可!这项工作本身比较简单,偏实用性的小尝试。不过结构相似性网络这个方向,我个人觉得还是值得进一步探索的。
您好!最近我在用 Morphometric INverse Divergence (MIND) 方法处理数据,用 recon-all 跑完皮层重建处理后,应用方法学作者开源的脚本使用freesurfer默认的 .annot 分割图谱(如aparc、aparc.a2009s)程序可以跑通,但我用非系统默认 .annot 文件 (从网络资源下载的如HCP Glasser-360的HCPMMP1.annot、Schaefer的Schaefer2018_400Parcels_7Networks_order.annot等)程序报错。报错信息为皮层指标与.annot文件顶点数目不一致(ValueError: could not broadcast input array from shape (137732,) into shape (163842,),get_vertex_df 函数报错)。我freesurfer版本为7.4.0,应用你们开发的BrainFex包跑皮层重建,我测试了我皮层重建后皮层指标顶点数为137732,我使用的.annot文件顶点数为163842(freesurfer跑完重建后背上label文件夹内的aparc、aparc.a2009s等文件顶点数为137732,与皮层指标顶点数一致),为标准皮层顶点数。我关注到你们最近发表的文章MIND versus MSN: A systematic evaluation of test–retest reliability and age sensitivity for T1-weighted structural similarity networks使用的是Schaefer300和DK308图谱,请问您是用什么方法获取到非系统自带的.annot文件,我这种报错该如何处理?感谢指点迷津!
报错的原因是MIND的计算是在个体皮层空间进行的(每个被试的顶点数都不一样),如果你提供标准皮层空间的annot文件(163842个顶点)肯定对应不上。如果要使用其他的分区模板,需要将标准皮层空间的annot文件投射到个体空间,然后再去计算MIND。具体的代码可以参考我公开的脚本:https://github.com/younghoo/paper-scripts/blob/main/Gao2025_MINDvsMSN/PREPROC/get_DK308_label.sh